Atípicos, apalancamiento e influencia
Introducción a la regresión en R

Richie Cotton
Data Evangelist at DataCamp
Datos de rutilo
roach <- fish %>%
filter(species == "Roach")
| species | length_cm | mass_g |
|---|---|---|
| Roach | 12.9 | 40 |
| Roach | 16.5 | 69 |
| Roach | 17.5 | 78 |
| Roach | 18.2 | 87 |
| Roach | 18.6 | 120 |
| ... | ... | ... |
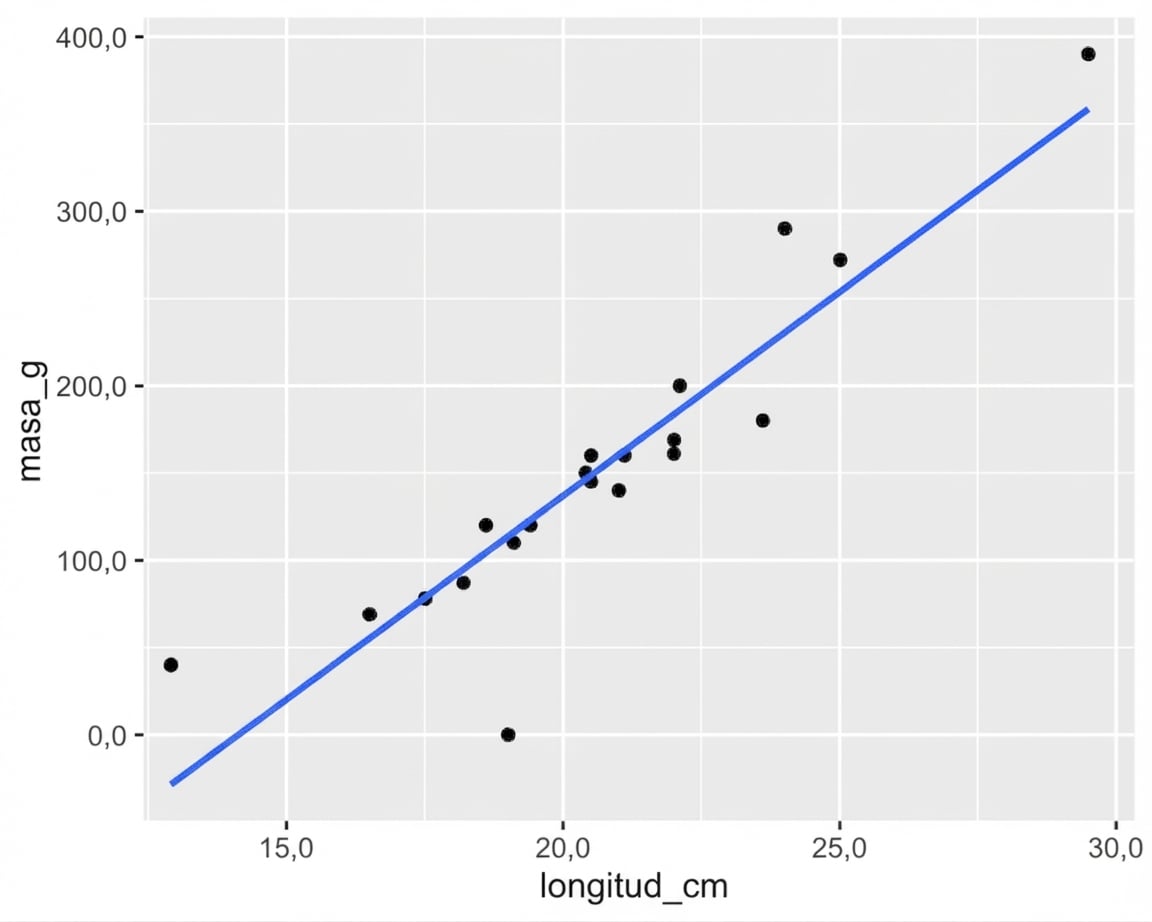
¿Qué puntos son atípicos?
ggplot(roach, aes(length_cm, mass_g)) +
geom_point() +
geom_smooth(method = "lm", se = FALSE)
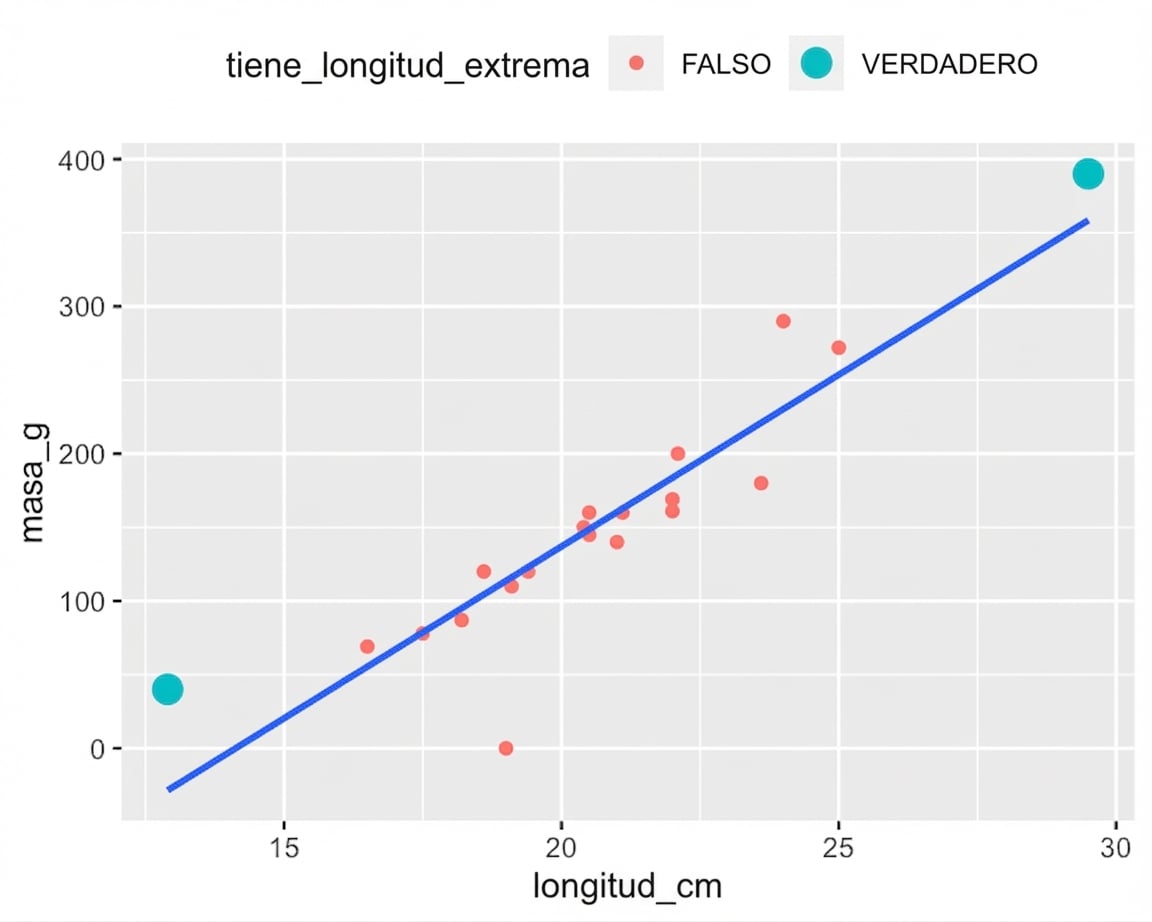
Valores explicativos extremos
roach %>%
mutate(
has_extreme_length = length_cm < 15 | length_cm > 26
) %>%
ggplot(aes(length_cm, mass_g)) +
geom_point(aes(color = has_extreme_length)) +
geom_smooth(method = "lm", se = FALSE)
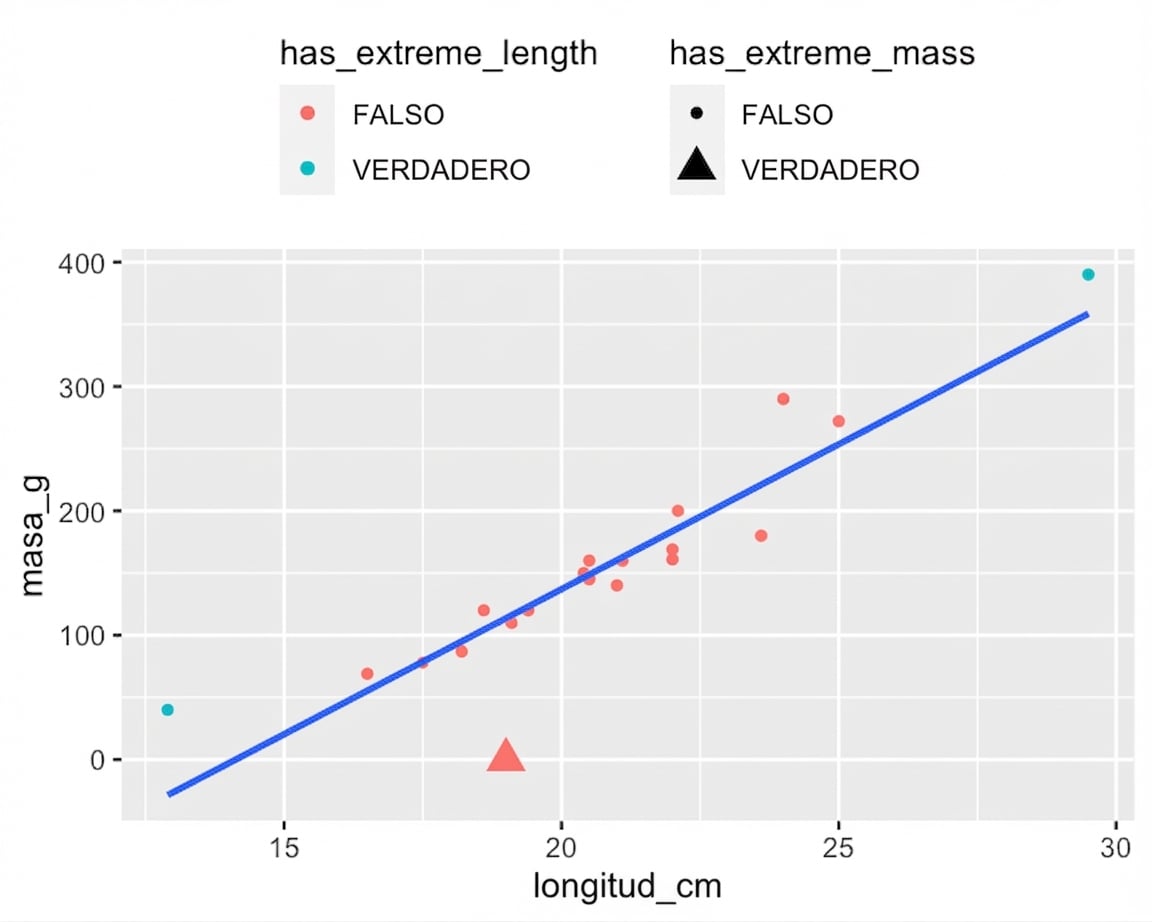
Valores de respuesta lejos de la recta de regresión
roach %>%
mutate(
has_extreme_length = length_cm < 15 | length_cm > 26,
has_extreme_mass = mass_g < 1
) %>%
ggplot(aes(length_cm, mass_g)) +
geom_point(
aes(
color = has_extreme_length,
shape = has_extreme_mass
)
) +
geom_smooth(method = "lm", se = FALSE)
Apalancamiento
El apalancamiento mide cuán extremos son los valores de la variable explicativa.
mdl_roach <- lm(mass_g ~ length_cm, data = roach)
hatvalues(mdl_roach)
1 2 3 4 5 6 7
0.3137 0.1255 0.0935 0.0763 0.0684 0.0619 0.0605
8 9 10 11 12 13 14
0.0568 0.0503 0.0501 0.0501 0.0506 0.0509 0.0581
15 16 17 18 19 20
0.0581 0.0593 0.0884 0.0995 0.1334 0.3947
La columna .hat
library(broom)
augment(mdl_roach)
# A tibble: 20 × 8
mass_g length_cm .fitted .resid .hat .sigma .cooksd .std.resid
<dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl>
1 40 12.9 -28.6 68.6 0.314 33.8 1.07 2.17
2 69 16.5 55.4 13.6 0.126 39.1 0.0104 0.381
3 78 17.5 78.7 -0.711 0.0935 39.3 0.0000197 -0.0196
4 87 18.2 95.0 -8.03 0.0763 39.2 0.00198 -0.219
5 120 18.6 104. 15.6 0.0684 39.1 0.00661 0.424
...
Rutilos con alto apalancamiento
mdl_roach %>%
augment() %>%
select(mass_g, length_cm, leverage = .hat) %>%
arrange(desc(leverage)) %>%
head()
# A tibble: 6 x 3
mass_g length_cm leverage
<dbl> <dbl> <dbl>
1 390 29.5 0.395 # rutilo muy largo
2 40 12.9 0.314 # rutilo muy corto
3 272 25 0.133
4 69 16.5 0.126
5 290 24 0.0995
6 78 17.5 0.0935
Influencia
La influencia mide cuánto cambiaría el modelo si quitaras la observación del conjunto al ajustar.

Distancia de Cook
La distancia de Cook es la medida de influencia más común.
cooks.distance(mdl_roach)
1 2 3 4 5 6
1.07e+00 1.04e-02 1.97e-05 1.98e-03 6.61e-03 3.12e-01
7 8 9 10 11 12
8.53e-04 1.99e-04 2.57e-04 2.56e-04 2.45e-03 7.95e-03
13 14 15 16 17 18
1.37e-04 4.82e-03 1.15e-02 4.52e-03 6.12e-02 1.50e-01
19 20
2.06e-02 3.66e-01
La columna .cooksd
library(broom)
augment(mdl_roach)
# A tibble: 20 x 9
mass_g length_cm .fitted .se.fit .resid .hat .sigma .cooksd .std.resid
<dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl>
1 40 12.9 -28.6 21.4 68.6 0.314 33.8 1.07 2.17
2 69 16.5 55.4 13.5 13.6 0.126 39.1 0.0104 0.381
3 78 17.5 78.7 11.7 -0.711 0.0935 39.3 0.0000197 -0.0196
4 87 18.2 95.0 10.5 -8.03 0.0763 39.2 0.00198 -0.219
5 120 18.6 104. 9.98 15.6 0.0684 39.1 0.00661 0.424
...
Rutilos más influyentes
mdl_roach %>%
augment() %>%
select(mass_g, length_cm, cooks_dist = .cooksd) %>%
arrange(desc(cooks_dist)) %>%
head()
# A tibble: 6 x 3
mass_g length_cm cooks_dist
<dbl> <dbl> <dbl>
1 40 12.9 1.07 # rutilo muy corto
2 390 29.5 0.366 # rutilo muy largo
3 0 19 0.312 # rutilo de masa cero
4 290 24 0.150
5 180 23.6 0.0612
6 272 25 0.0206
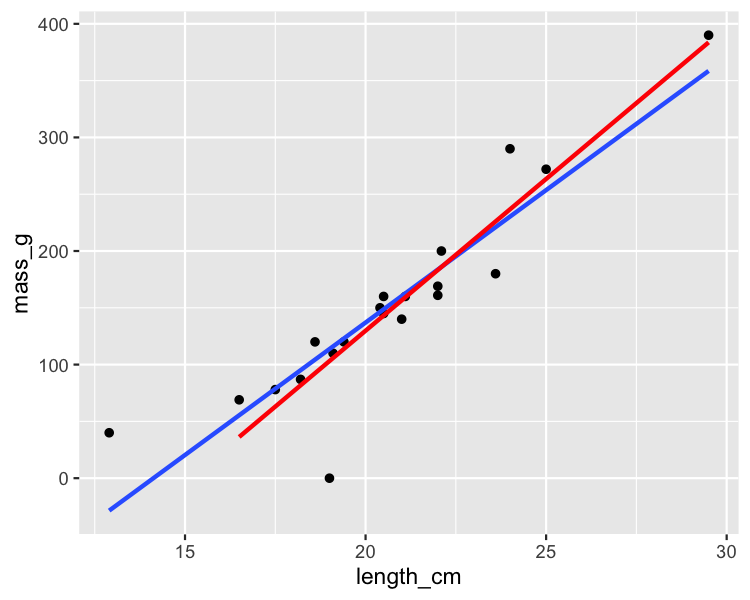
Quitando el rutilo más influyente
roach_not_short <- roach %>%
filter(length != 12.9)
ggplot(roach, aes(length_cm, mass_g)) +
geom_point() +
geom_smooth(method = "lm", se = FALSE) +
geom_smooth(
method = "lm", se = FALSE,
data = roach_not_short, color = "red"
)
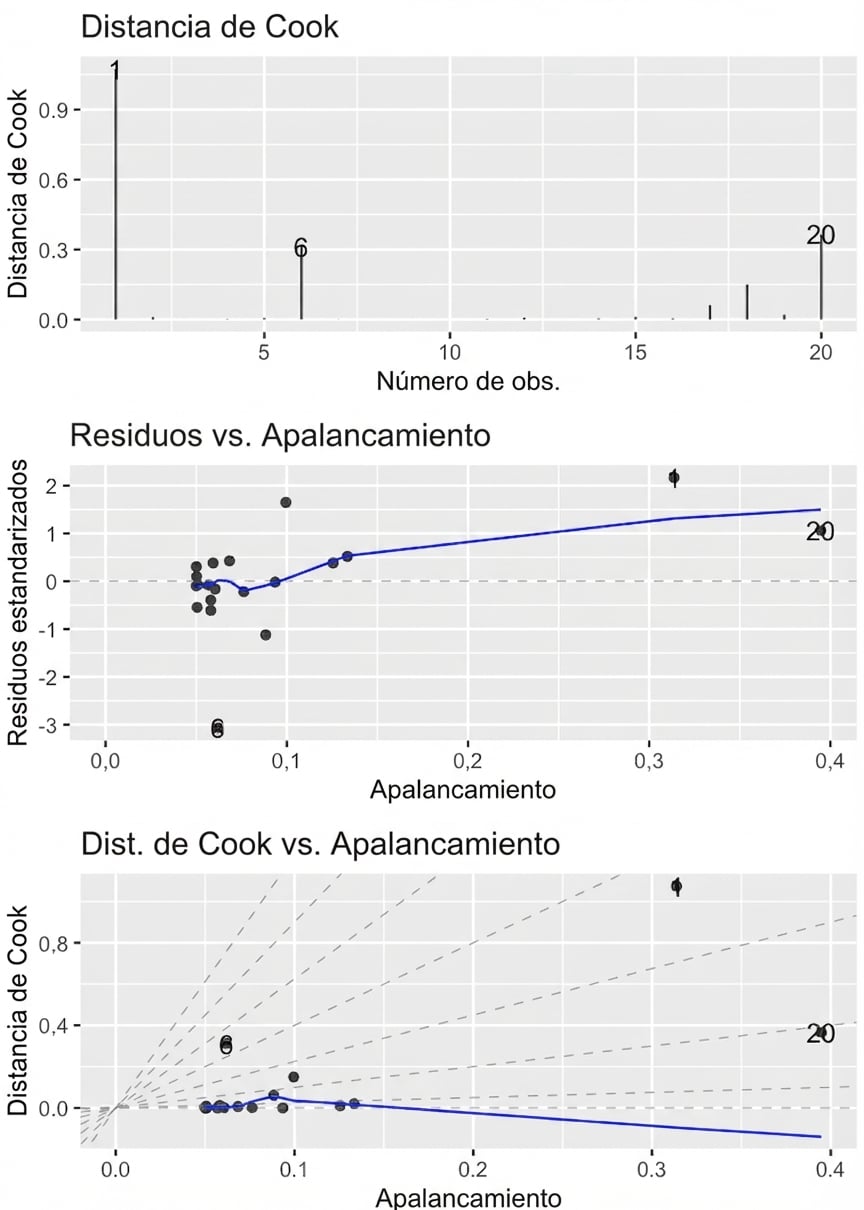
autoplot()
autoplot(
mdl_roach,
which = 4:6,
nrow = 3,
ncol = 1
)
¡Vamos a practicar!
Introducción a la regresión en R

