Dimensies verminderen
Feature engineering in R

Jorge Zazueta
Research Professor and Head of the Modeling Group at the School of Economics, UASLP
Kenmerken met nulvariantie
Sommige datasets hebben kolommen met constante waarden of nulvariantie. We kunnen die kenmerken filteren met step_zv() in onze recipe().
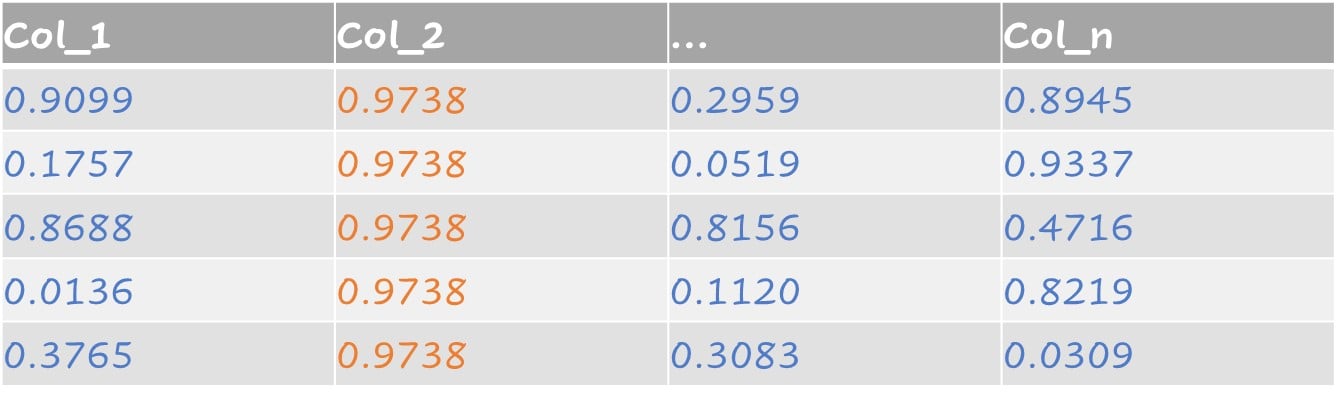
Kenmerken met bijna nulvariantie
Kenmerken met bijna nulvariantie zijn voorspellers met één waarde én voorspellers met beide eigenschappen hieronder:
Heel weinig unieke waarden vergeleken met het aantal samples
De verhouding tussen de frequentie van de meest voorkomende waarde en die van de op één na meest voorkomende is groot
Voorbeeld van bijna nulvariantie:
- Bij 100 observaties zijn er twee waarden, maar één komt maar één keer voor.
step_nzv() vindt en verwijdert voorspellers met deze eigenschappen.
Principal Component Analysis (PCA)
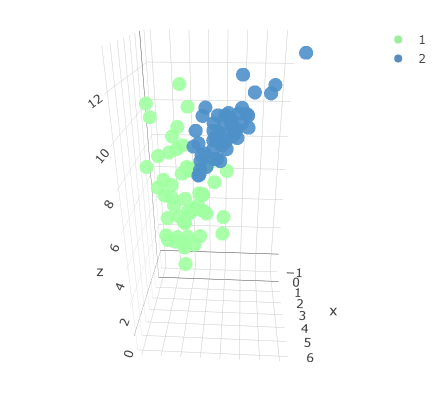
Oorspronkelijke driedimensionale dataset met twee klassen.
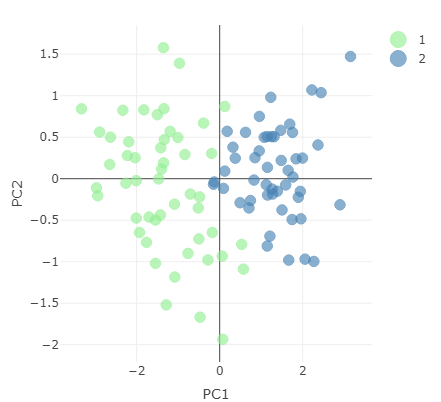
Gereduceerde dataset met de eerste twee hoofdcomponenten.
Laten we een recipe preppen
Een recipe maken voor PCA en de output ophalen met prep().
pc_recipe <-
recipe(~., data = loans_num) %>%
step_nzv(all_numeric()) %>%
step_normalize(all_numeric()) %>%
step_pca(all_numeric())
pca_output <- prep(pc_recipe)
We kunnen de beschikbare info bekijken met names() op pca_output.
names(pca_output)
[1] "var_info" "term_info"
[3] "steps" "template"
[5] "levels" "retained"
[7] "requirements" "tr_info"
[9] "orig_lvls" "last_term_info"
Verklaarde variantie vinden
Haal de standaarddeviatie uit het object pca_output en bereken de verklaarde variantie.
stdv <- pca_output$steps[[3]]$res$sdev
var_explained <- stdv^2/sum(stdv^2)
PCA = tibble(PC = 1:length(stdv),
var_explained = var_explained,
cumulative = cumsum(var_explained))
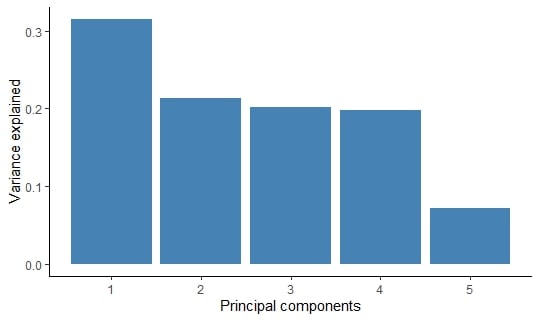
Een tabel met de verklaarde variantie per hoofdcomponent.
# A tibble: 5 × 3
PC var_explained cumulative
<int> <dbl> <dbl>
1 1 0.315 0.315
2 2 0.214 0.529
3 3 0.202 0.730
4 4 0.198 0.928
5 5 0.0722 1
Verklaarde variantie visualiseren
We kunnen de output als kolomgrafiek plotten met ggplot2.
PCA %>%
ggplot(aes(x = PC,
y = var_explained)) +
geom_col(fill = "steelblue") +
xlab("Principal components") +
ylab("Variance explained")
Verklaarde variantie per hoofdcomponent.
Laten we oefenen!
Feature engineering in R

