De voordelen meten
Parallel programmeren in R

Nabeel Imam
Data Scientist
Speelvoorbeeld
numbers <- 1:1000000# Sequentieel sqroots <- lapply(numbers, sqrt)# Parallel cl <- makeCluster(4) sqroots <- parLapply(cl, numbers, sqrt) stopCluster(my_cluster)
Welke is sneller?
Performance benchmarken
Voer code meerdere keren uit om de gemiddelde uitvoeringstijd te schatten
library(microbenchmark)microbenchmark( "Sequential" = lapply(numbers, sqrt),"Parallel" = { cl <- makeCluster(4) parLapply(cl, numbers, sqrt) stopCluster(my_cluster) },times = 10 )
Unit: milliseconds
expr min mean max neval
Sequential 633.96 838.09 993.59 10
Parallel 1136.95 1247.29 1557.58 10
- Simpele numerieke operaties profiteren zelden van parallelisatie
- Profiling geeft regels-rapport; benchmarking geeft totale tijden
De olifant in de kamer
sqroots <- sqrt(numbers)

Vectorisatie
sqroots <- sqrt(numbers)
- Basis-R-functies, zoals
sqrt(), zijn gevectoriseerd. - Pas één functie toe op veel inputs
- Zeer snel maar alleen voor eenvoudige bewerkingen
microbenchmark(
"Vectorized" = sqrt(numbers),
"Sequential" = lapply(numbers, sqrt),
"Parallel" = {
cl <- makeCluster(4)
parLapply(cl, numbers, sqrt)
stopCluster(my_cluster)
},
times = 10)
Unit: milliseconds
expr min mean max neval
Vectorized 2.3904 9.2071 66.303 10
Sequential 352.1166 771.7491 1004.753 10
Parallel 1191.3176 1377.6926 1700.316 10
De bootstrap
Steekproeven trekken uit de huidige data met teruglegging
print(ls_df)
$`2001`
Country Life_expectancy Year
1 Afghanistan 56.3 2001
2 Albania 74.3 2001
3 Algeria 71.1 2001
...
$`2002`
Country Life_expectancy Year
1 Afghanistan 56.8 2002
2 Albania 74.6 2002
3 Algeria 71.6 2002
...
Klassieke versie
df <- ls_df$`2001`estimates <- rep(0, 10000)for (i in 1:10000) { b <- sample(df$Life_expectancy, replace = T)estimates[i] <- mean(b) }
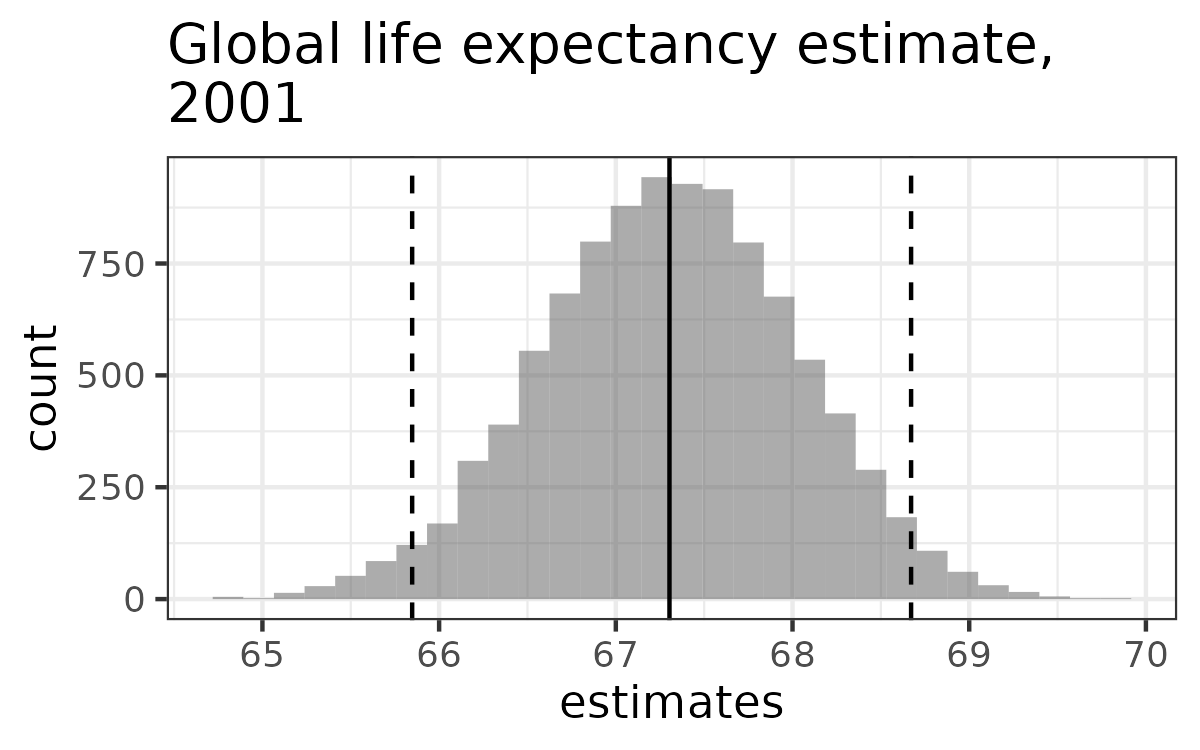
- Betrouwbaarheidsinterval via kwantielen:
quantile(estimates, c(0.025, 0.975))
Goed nieuws
Bootstraps kun je paralleliseren
estimates <- rep(0, 10000)
for (i in 1:10000) {
b <- sample(df$Life_expectancy,
replace = T)
estimates[i] <- mean(b)
}
boot_dist <- function (df) { estimates <- rep(0, 10000) for (i in 1:10000) { b <- sample(df$Life_expectancy, replace = T) estimates[i] <- mean(b) } return(estimates) }cl <- makeCluster(4) ls_dists <- parLapply(cl, ls_df, boot_dist) stopCluster(cl)
De voordelen
microbenchmark(
"lapply" = lapply(ls_df, boot_dist),
"parLapply" = {
cl <- makeCluster(4)
parLapply(cl, ls_df, boot_dist)
stopCluster(cl)
},
times = 10
)
Unit: seconds
expr min mean max neval
lapply 3.6938 4.2184 4.5267 10
parLapply 1.9006 2.5166 2.7292 10
Hoe kom je daar:
- Profiler je code, vind het traagste deel
- Paralleliseer/optimaliseer die stap
- Benchmark en vergelijk
Laten we oefenen!
Parallel programmeren in R

