Evaluatie van eindmodellen
R voor SAS-gebruikers

Melinda Higgins, PhD
Research Professor/Senior Biostatistician Emory University
Eindopdrachten
Cursusafsluiting
Voer regressiemodellen uit
- voor verschillende voorspellers
- voor verschillende groepen
Kies beste modellen
- sla modelresultaten op
- extraheer en toon fitstatistieken
Laat je skills zien
Evalueer en vergelijk modellen
- met grafische visualisaties
Rapporteer beste verbanden
- tussen variabelen
- totaal en per groep
Modellen vergelijken
# Run lm() voor diffht op bmi, sla model op
lmdiffhtbmi <- lm(diffht ~ bmi,
data = daviskeep)
# Run lm() voor diffht op weight, sla model op
lmdiffhtwt <- lm(diffht ~ weight,
data = daviskeep)
# Run summary() voor elk model, sla resultaten op
smrylmdiffhtbmi <- summary(lmdiffhtbmi)
smrylmdiffhtwt <- summary(lmdiffhtwt)
Modellen vergelijken
# Toon r.squared voor gewichtmodel
smrylmdiffhtwt$r.squared
# Toon r.squared voor BMI-model
smrylmdiffhtbmi$r.squared
# Vergelijk AIC's voor beide modellen
AIC(lmdiffhtbmi, lmdiffhtwt)
[1] 0.003281645
[1] 0.00121824
df AIC
lmdiffhtbmi 3 788.0816
lmdiffhtwt 3 787.7052
Modellen per groep - mannen vs. vrouwen
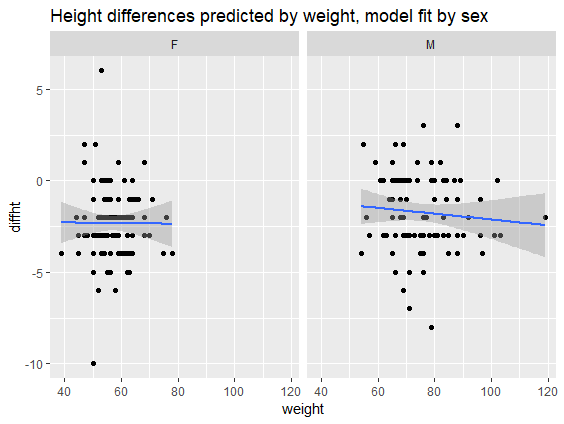
# Plot diffht op weight, per sex
ggplot(daviskeep,
aes(diffht, weight)) +
geom_point() +
geom_smooth(method = "lm") +
facet_wrap(vars(sex)) +
ggtitle("Hoogteverschillen
voorspeld door gewicht,
modelfit per geslacht")
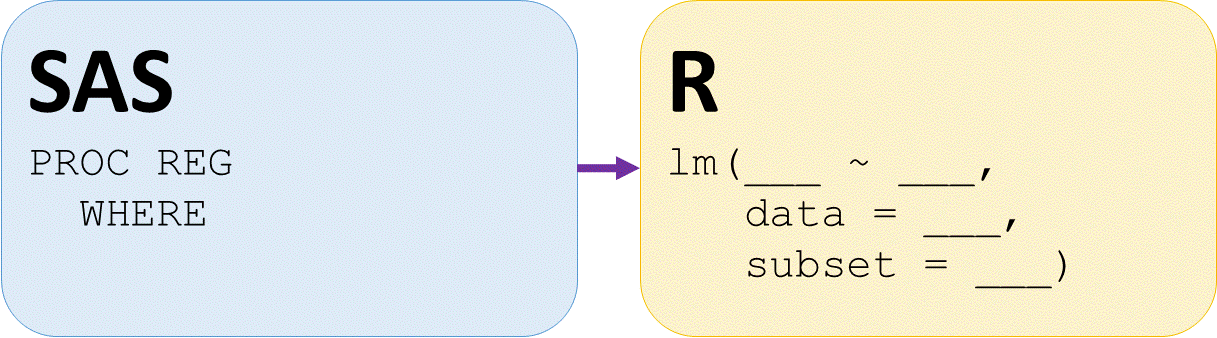
Regressie op subset

Modellen fitten voor subsets
# lm() van diffht op weight voor vrouwen
lmdiffhtwtF <- lm(diffht ~ weight,
subset = (sex == "F"),
data = daviskeep)
# lm() van diffht op weight voor mannen
lmdiffhtwtM <- lm(diffht ~ weight,
subset = (sex == "M"),
data = daviskeep)
# Run summary() voor elk model en sla op
smrylmdiffhtwtF <- summary(lmdiffhtwtF)
smrylmdiffhtwtM <- summary(lmdiffhtwtM)
Modellen fitten voor subsets
# r.squared voor model alleen vrouwen
smrylmdiffhtwtF$r.squared
# r.squared voor model alleen mannen
smrylmdiffhtwtM$r.squared
[1] 4.00807e-05
[1] 0.00804139
Laten we afsluiten met een paar modellen om abalone-leeftijden te voorspellen!
R voor SAS-gebruikers

