Correlaties en t-toetsen
R voor SAS-gebruikers

Melinda Higgins, PhD
Research Professor/Senior Biostatistician Emory University
Correlaties: SAS vs. R

Correlaties met het psych-pakket
# Correlaties met psych::corr.test()
daviskeep %>%
select(bmi, weight, height) %>%
psych::corr.test()
Call:psych::corr.test(x = .)
Correlation matrix
bmi weight height
bmi 1.00 0.88 0.38
weight 0.88 1.00 0.77
height 0.38 0.77 1.00
Sample Size
[1] 199
Probability values (Entries above the
diagonal are adjusted for multiple tests.)
bmi weight height
bmi 0 0 0
weight 0 0 0
height 0 0 0
Scatterplotmatrix in SAS en R

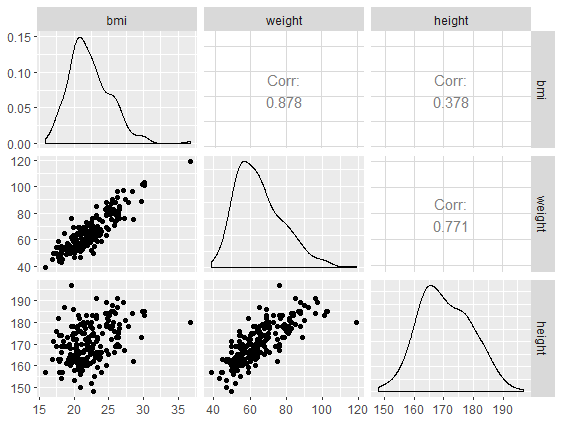
Scatterplotmatrix - functie GGally::ggpairs()
# Matrixplot met GGally::ggpairs()
daviskeep %>%
select(bmi, weight, height) %>%
GGally::ggpairs()
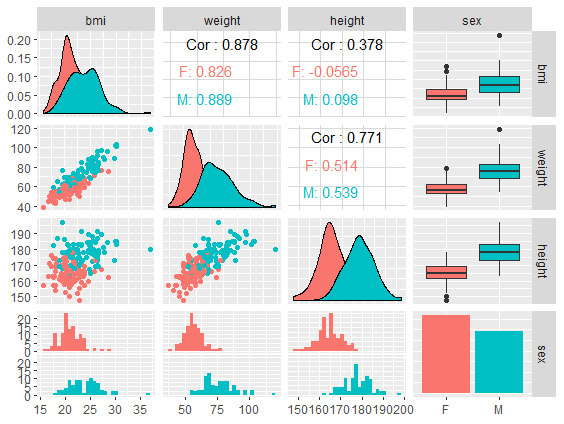
Scatterplotmatrix - ggpairs per groep
# Kleur punten per geslachtsgroep
daviskeep %>%
select(bmi, weight, height, sex) %>%
GGally::ggpairs(aes(color = sex))
Beschrijvende statistiek per groep
Zonder groepsaantallen
# Gemiddelde en sd voor bmi per geslacht
daviskeep %>% group_by(sex) %>%
select(sex, bmi) %>%
summarise(across(everything(),
list(mean = ~ mean(.x),
sd = ~ sd(.x))))
# A tibble: 2 × 3
sex bmi_mean bmi_sd
<fct> <dbl> <dbl>
1 F 21.0 2.18
2 M 23.9 3.12
Met groepsaantallen
# Voeg N = n() toe; gemiddelde en sd voor bmi per geslacht
daviskeep %>% group_by(sex) %>%
select(sex, bmi) %>%
summarise(across(everything(),
list(mean = ~ mean(.x),
sd = ~ sd(.x))),
N = n())
# A tibble: 2 × 4
sex bmi_mean bmi_sd N
<fct> <dbl> <dbl> <int>
1 F 21.0 2.18 111
2 M 23.9 3.12 88
1 https://dplyr.tidyverse.org/reference/context.html
t-toetsen in SAS en R



t-toetsen - controleer gelijke varianties
# Test op gelijke varianties
var.test(bmi ~ sex, data = daviskeep)
F test to compare two variances
data: bmi by sex
F = 0.48637, num df = 110, denom df = 87, p-value = 0.0003668
alternative hypothesis: true ratio of variances is not equal to 1
95 percent confidence interval:
0.3244691 0.7221946
sample estimates:
ratio of variances
0.4863699
t-toetsen - gepoold en ongepoold
# ONGEPOOLDE t-toets: bmi per geslacht
t.test(bmi ~ sex,
data = daviskeep)
Welch Two Sample t-test
data: bmi by sex
t = -7.5158, df = 149.45,
p-value = 4.819e-12
alternative hypothesis: true difference
in means is not equal to 0
95 percent confidence interval:
-3.716353 -2.169035
sample estimates:
mean in group F mean in group M
20.95632 23.89901
# GEPOOLDE t-toets: bmi per geslacht
t.test(bmi ~ sex, data = daviskeep,
var.equal = TRUE)
Two Sample t-test
data: bmi by sex
t = -7.8239, df = 197,
p-value = 3.055e-13
alternative hypothesis: true difference
in means is not equal to 0
95 percent confidence interval:
-3.684428 -2.200960
sample estimates:
mean in group F mean in group M
20.95632 23.89901
Laten we bivariate relaties in abalones verkennen!
R voor SAS-gebruikers

