Come far crescere il tuo albero
Machine Learning con modelli ad albero in R

Sandro Raabe
Data Scientist
Dataset Diabetes
head(diabetes)
# A tibble: 6 x 9
outcome pregnancies glucose blood_pressure skin_thickness insulin bmi age
<fct> <int> <int> <int> <int> <int> <dbl> <int>
1 yes 6 148 72 35 0 33.6 50
2 no 1 85 66 29 0 26.6 31
3 yes 8 183 64 0 0 23.3 32
Usare l’intero dataset
- Hai usato tutti i dati per il training: non restano dati per testare il modello

Divisione dei dati
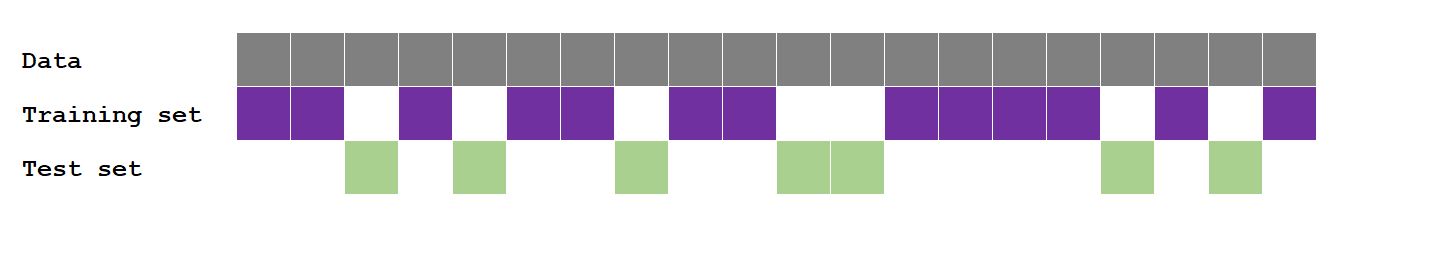

Metodi di split



La funzione initial_split()
- Divide i dati in modo casuale in un solo training set e un solo test set
# Suddividi i dati in proporzione (default: 0.75)
diabetes_split <- initial_split(diabetes, prop = 0.9)
diabetes_split
<Analysis/Assess/Total>
<692/76/768>
1 dal pacchetto rsample
Funzioni training() e testing()
- Estrai training e test set da uno split dei dati
diabetes_train <- training(diabetes_split)diabetes_test <- testing(diabetes_split)
- Verifica:
nrow(diabetes_train)/nrow(diabetes)
[1] 0.9007812
1 da rsample
Evita squilibri di classe
# Conteggio nel training degli esiti 'yes' e 'no'
counts_train <- table(diabetes_train$outcome)
counts_train
no yes
490 86
# Proporzione di 'yes' nel training
prop_yes_train <- counts_train["yes"]/
sum(counts_train)
prop_yes_train
0.15
# Conteggio nel test degli esiti 'yes' e 'no'
counts_test <- table(diabetes_test$outcome)
counts_test
no yes
28 48
# Proporzione di 'yes' nel test
prop_yes_test <- counts_test["yes"]/
sum(counts_test)
prop_yes_test
0.63
Soluzione: imporsi distribuzioni simili
initial_split(diabetes,
prop = 0.9,
strata = outcome)
- Garantisce uno split casuale con distribuzione simile della variabile
outcome
Facciamo lo split!
Machine Learning con modelli ad albero in R

