Monitorare e gestire la memoria
Programmazione parallela in R

Nabeel Imam
Data Scientist
Coda e spazio

Il flusso parallelo

Il flusso parallelo

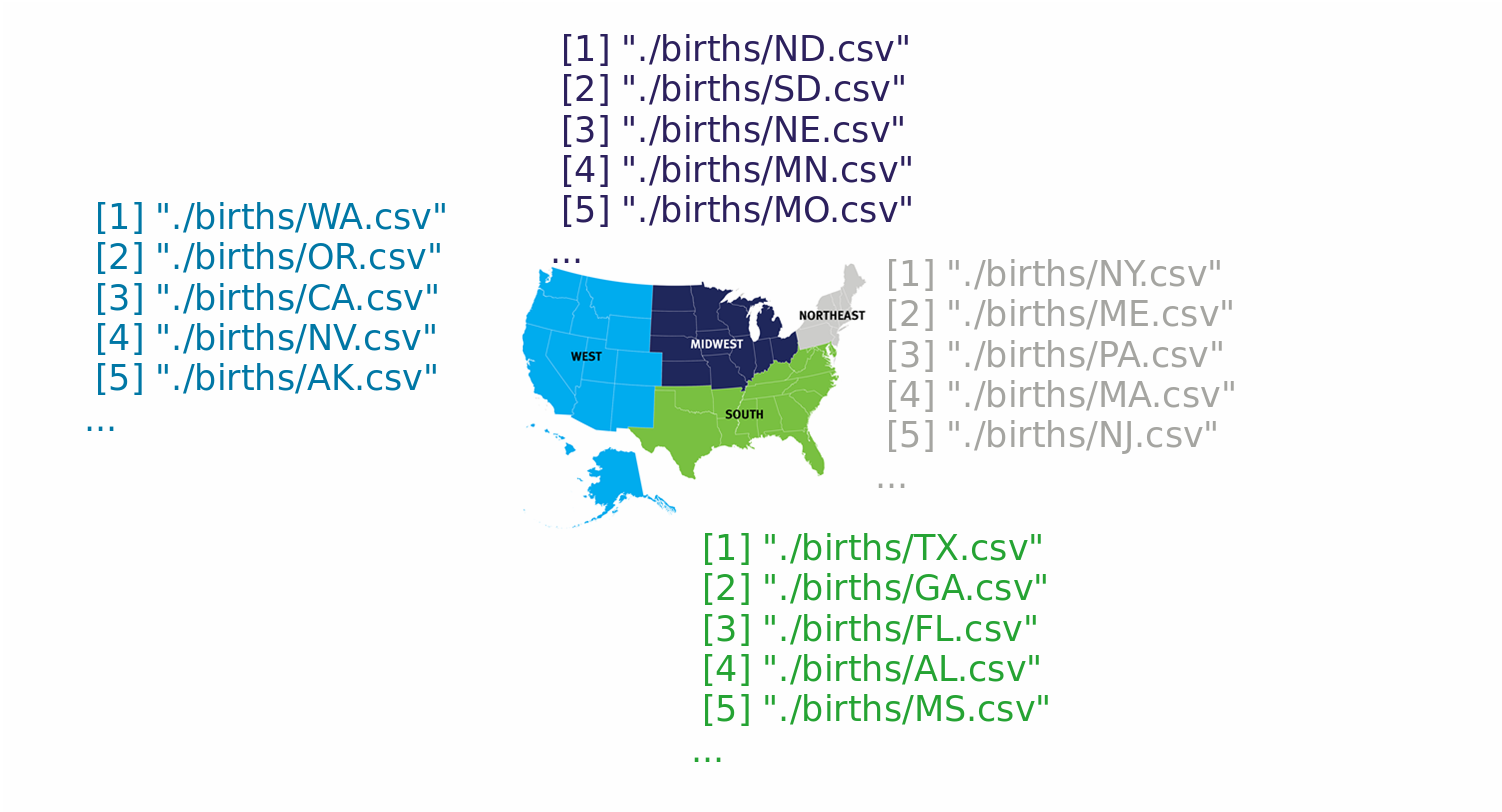
I dati sulle nascite
print(ls_files)
[1] "./births/AK.csv"
[2] "./births/AL.csv"
[3] "./births/AR.csv"
[4] "./births/AZ.csv"
[5] "./births/CA.csv"
[6] "./births/CO.csv"
[7] "./births/CT.csv"
[8] "./births/DC.csv"
[9] "./births/DE.csv"
[10] "./births/FL.csv"
...
Mappare con futures
plan(multisession, workers = 2)ls_df <- future_map(ls_files, read.csv)plan(sequential)print(ls_df)
[[1]]
state month plurality weight_gain_pounds mother_age
AK 1 1 30 43
...
[[2]]
state month plurality weight_gain_pounds mother_age
AL 10 1 60 33
...
...
Profiling con due worker
profvis({
plan(multisession, workers = 2)
ls_df <- future_map(ls_files, read.csv)
plan(sequential)
})

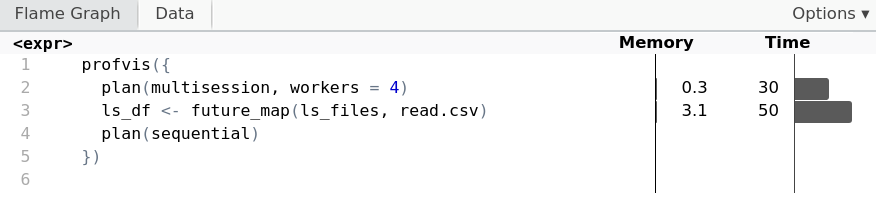
Profiling con quattro worker
profvis({
plan(multisession, workers = 4)
ls_df <- future_map(ls_files, read.csv)
plan(sequential)
})
Dietro le quinte
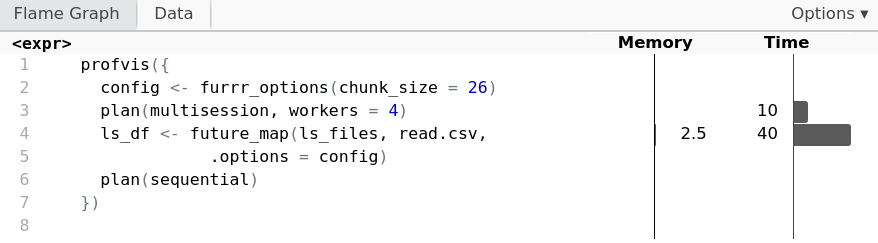
Gestire la memoria con chunk
config <- furrr_options(chunk_size = 26)plan(multisession, workers = 4) ls_df <- future_map(ls_files, read.csv,.options = config) plan(sequential)
Gestire la memoria con chunk
profvis({
config <- furrr_options(chunk_size = 26)
plan(multisession, workers = 4)
ls_df <- future_map(ls_files, read.csv,
.options = config)
plan(sequential)
})
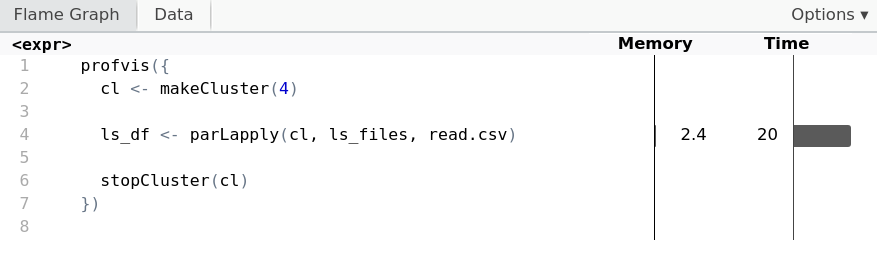
Chunk con parallel
cl <- makeCluster(4)ls_df <- parLapply(cl, ls_files, read.csv)stopCluster(cl)
Chunk con parallel
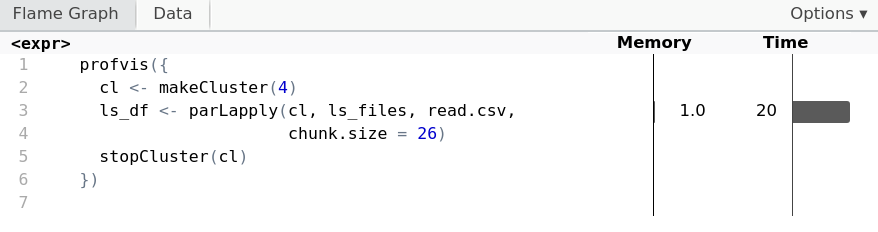
cl <- makeCluster(4) ls_df <- parLapply(cl, ls_files, read.csv,chunk.size = 26)stopCluster(cl)
Quando fare chunking?
- Il chunking è già ottimale di default
- Con oggetti grandi e poca memoria
- Prova con meno core, se possibile
- Sperimenta alcune dimensioni dei chunk per ottimizzare
Passons à la pratique !
Programmazione parallela in R

