Valutazione dei modelli finali
R per utenti SAS

Melinda Higgins, PhD
Research Professor/Senior Biostatistician Emory University
Esercizi finali
Conclusione del corso
Esegui modelli di regressione
- con predittori diversi
- per gruppi diversi
Scegli i modelli migliori
- salva i risultati
- estrai e mostra le statistiche di fit
Metti in mostra le tue skill
Valuta e confronta i modelli
- con visualizzazioni grafiche
Riporta le associazioni migliori
- tra variabili
- globali e per gruppo
Confronto tra modelli
# Esegui lm() per diffht ~ bmi, salva il modello
lmdiffhtbmi <- lm(diffht ~ bmi,
data = daviskeep)
# Esegui lm() per diffht ~ weight, salva il modello
lmdiffhtwt <- lm(diffht ~ weight,
data = daviskeep)
# Esegui summary() per ogni modello, salva i risultati
smrylmdiffhtbmi <- summary(lmdiffhtbmi)
smrylmdiffhtwt <- summary(lmdiffhtwt)
Confronto tra modelli
# Mostra r.squared per il modello con weight
smrylmdiffhtwt$r.squared
# Mostra r.squared per il modello con bmi
smrylmdiffhtbmi$r.squared
# Confronta gli AIC di entrambi i modelli
AIC(lmdiffhtbmi, lmdiffhtwt)
[1] 0.003281645
[1] 0.00121824
df AIC
lmdiffhtbmi 3 788.0816
lmdiffhtwt 3 787.7052
Modelli per gruppo - uomini vs donne
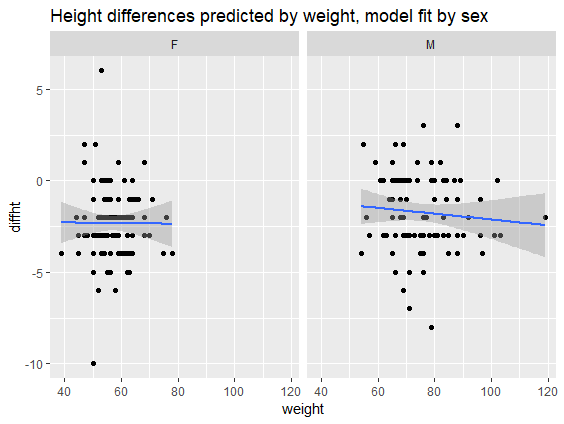
# Grafica diffht vs weight per sesso
ggplot(daviskeep,
aes(diffht, weight)) +
geom_point() +
geom_smooth(method = "lm") +
facet_wrap(vars(sex)) +
ggtitle("Differenze di altezza
previste da weight,
modello per sesso")
Regressione su sottoinsieme
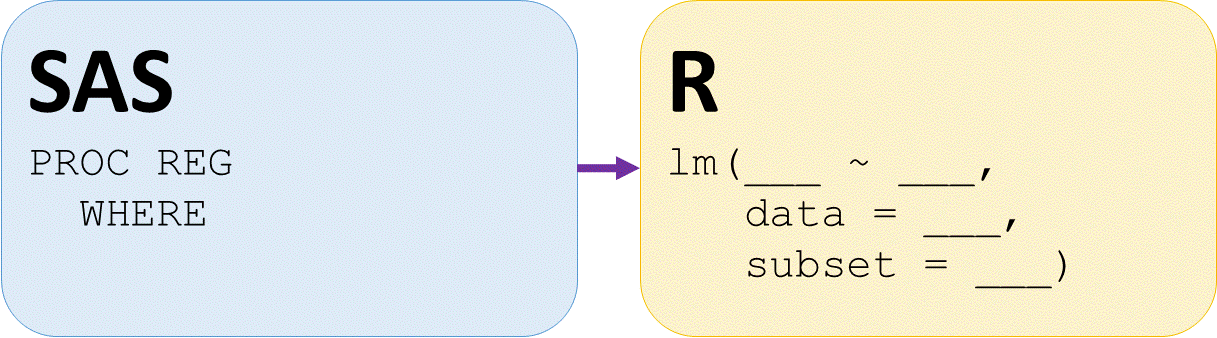

Adatta modelli per sottoinsiemi
# lm() di diffht in funzione di weight per femmine
lmdiffhtwtF <- lm(diffht ~ weight,
subset = (sex == "F"),
data = daviskeep)
# lm() di diffht in funzione di weight per maschi
lmdiffhtwtM <- lm(diffht ~ weight,
subset = (sex == "M"),
data = daviskeep)
# Esegui summary() per ogni modello e salva i risultati
smrylmdiffhtwtF <- summary(lmdiffhtwtF)
smrylmdiffhtwtM <- summary(lmdiffhtwtM)
Adatta modelli per sottoinsiemi
# r.squared per il modello solo femmine
smrylmdiffhtwtF$r.squared
# r.squared per il modello solo maschi
smrylmdiffhtwtM$r.squared
[1] 4.00807e-05
[1] 0.00804139
Concludiamo sviluppando alcuni modelli per prevedere l’età degli abalone!
R per utenti SAS

