Qualità dei dati e pulizia
R per utenti SAS

Melinda Higgins, PhD
Research Professor/Senior Biostatistician Emory University
Controlla le distribuzioni
# Continua con davismod
davismod %>%
head(5)
sex weight height repwt repht bmi diffht difflow bmicat
1 M 77 182 77 180 23.24598 -2 FALSE 1. underwt/norm
2 F 58 161 51 159 22.37568 -2 FALSE 1. underwt/norm
3 F 53 161 54 158 20.44674 -3 TRUE 1. underwt/norm
4 M 68 177 70 175 21.70513 -2 FALSE 1. underwt/norm
5 F 59 157 59 155 23.93606 -2 FALSE 1. underwt/norm
Controlla le distribuzioni
# Statistiche riassuntive per bmi: min, max, mediana
davismod %>%
pull(bmi) %>%
summary()
Min. 1st Qu. Median Mean 3rd Qu. Max.
15.82 20.23 21.84 24.70 23.94 510.93
Nota che Max. > 500
Visualizza le distribuzioni
# Crea un dotplot del bmi con geom_dotplot()
ggplot(davismod, aes(bmi)) +
geom_dotplot()
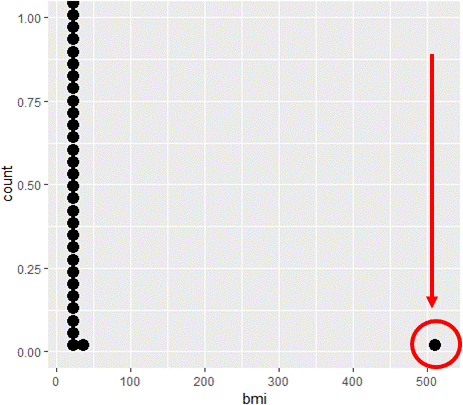
Trova gli outlier
# Ordina i dati con arrange(), vedi le ultime 6 righe con tail()
davismod %>%
arrange(bmi) %>%
tail()
sex weight height repwt repht bmi diffht difflow bmicat
195 M 89 173 86 173 29.73704 0 FALSE 2. overwt
196 M 102 185 107 185 29.80278 0 FALSE 2. overwt
197 M 103 185 101 182 30.09496 -3 TRUE 3. obese
198 M 101 183 100 180 30.15916 -3 TRUE 3. obese
199 M 119 180 124 178 36.72840 -2 FALSE 3. obese
200 F 166 57 56 163 510.92644 106 FALSE 3. obese
Visualizza l’assunzione peso <= altezza
# Scatterplot con retta di riferimento y=x
ggplot(davismod,
aes(weight, height)) +
geom_point() +
geom_abline(intercept=0, slope=1)
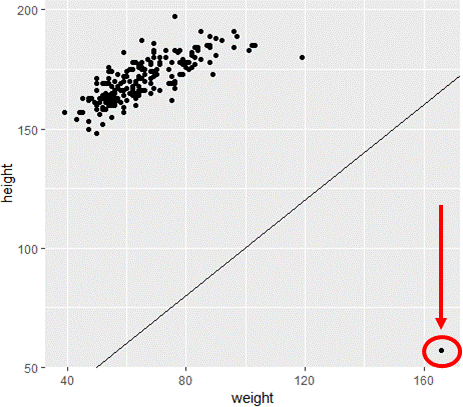
Filtra i casi con errori
# Usa filter() di dplyr, tieni i casi con bmi < 100
daviskeep <- davismod %>%
filter(bmi < 100)
# Vedi le ultime 6 righe
daviskeep %>%
arrange(bmi) %>%
tail()
sex weight height repwt repht bmi diffht difflow bmicat
194 F 75 162 75 158 28.57796 -4 TRUE 2. overwt
195 M 89 173 86 173 29.73704 0 FALSE 2. overwt
196 M 102 185 107 185 29.80278 0 FALSE 2. overwt
197 M 103 185 101 182 30.09496 -3 TRUE 3. obese
198 M 101 183 100 180 30.15916 -3 TRUE 3. obese
199 M 119 180 124 178 36.72840 -2 FALSE 3. obese
Visualizza il bmi corretto
# Dotplot del bmi
ggplot(daviskeep, aes(bmi)) +
geom_dotplot()
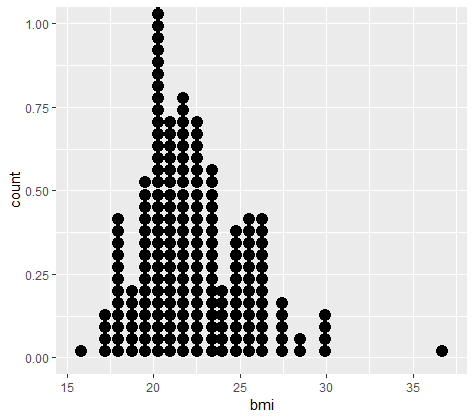
Pulizia finale del dataset abalone
- Controlla le assunzioni del dataset abalone
- Rimuovi i casi che le violano
- Finalizza il dataset per analisi e modelli
ASSUNZIONI:
- Tutte le misure devono essere > 0
lengthè la dimensione massima del guscioheightediameter<lengthwholeWeightè il peso totale- Gli altri pesi <
wholeWeight

Esploriamo e puliamo il dataset abalone
R per utenti SAS

