Imputazione multipla con bootstrap
Gestione dei dati mancanti con imputazioni in R

Michal Oleszak
Machine Learning Engineer
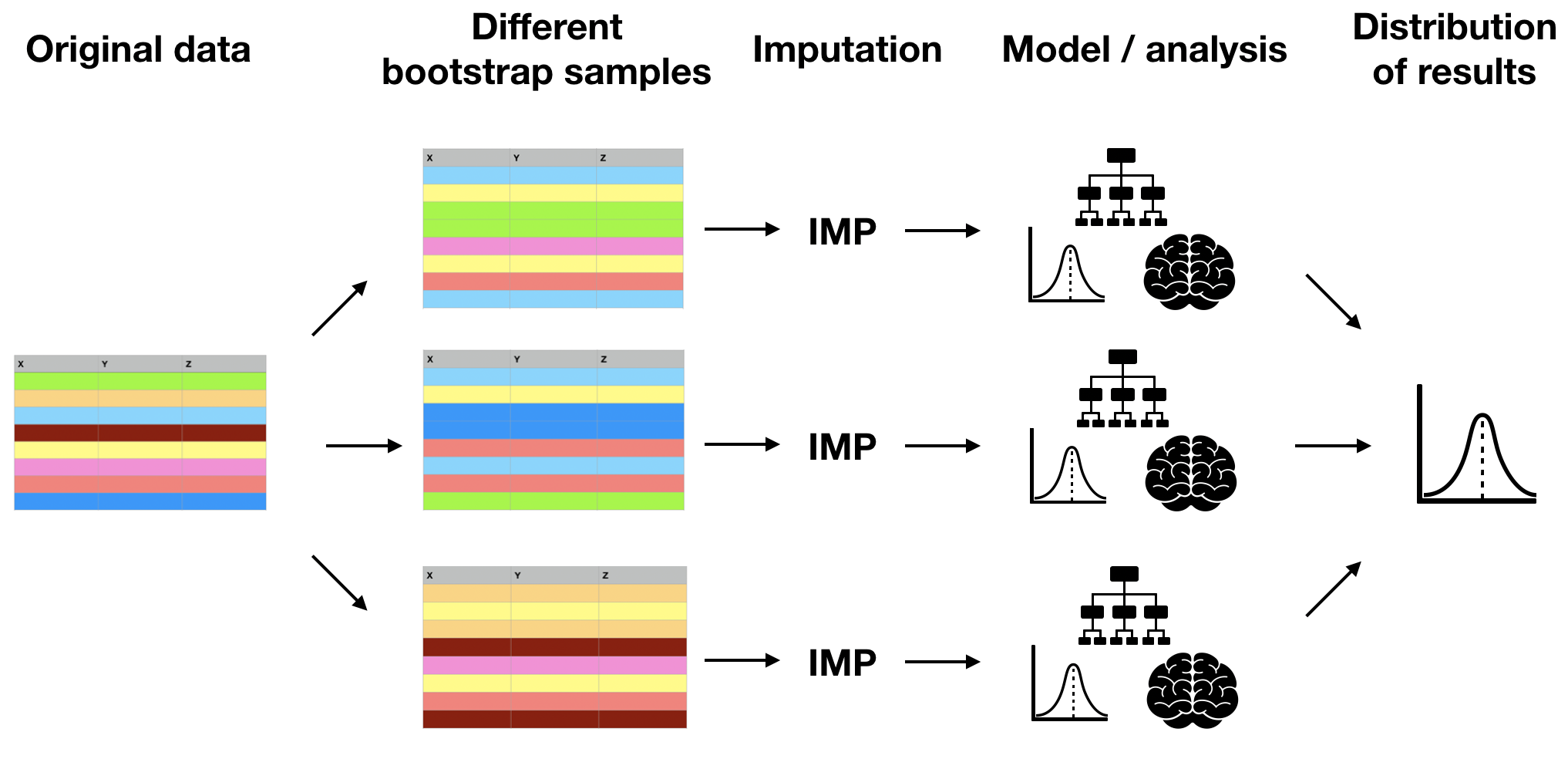
Incertezza dall'imputazione
- L'imputazione è di solito il primo passo prima di analisi o modellazione.
- I valori mancanti sono stimati con incertezza.
- Questa incertezza va considerata in ogni analisi su dati imputati.

In quasi metà degli studi, i risultati chiave scompaiono
Bootstrap
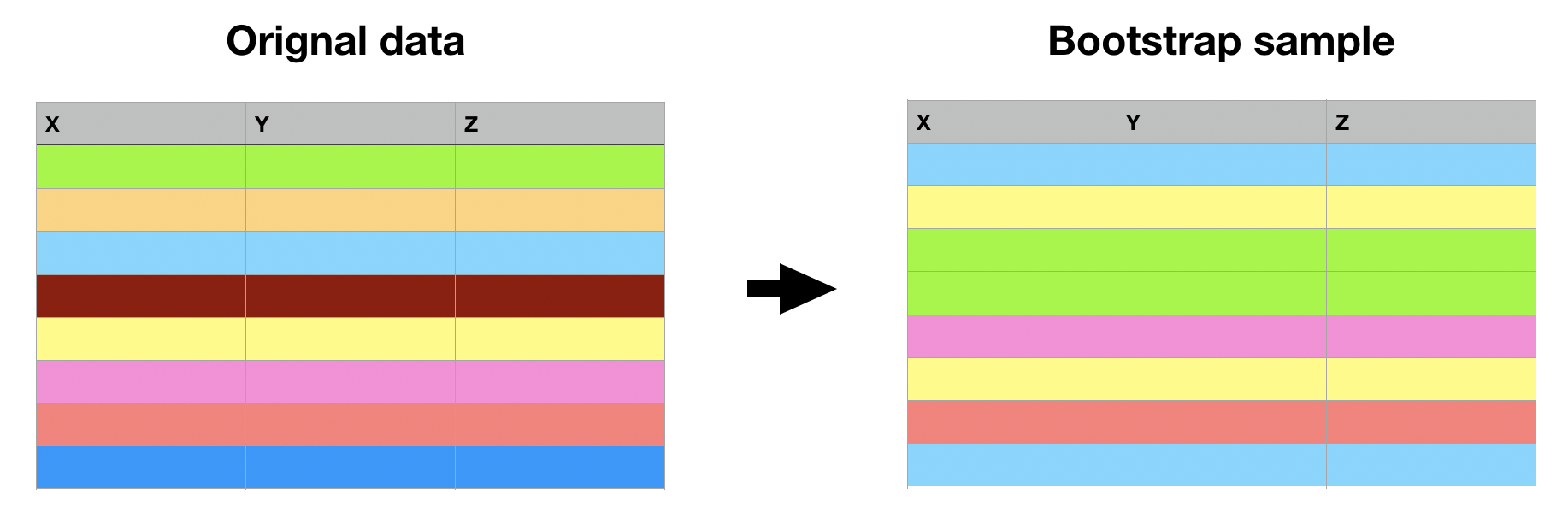
Bootstrap = campionare righe con reinserimento per ottenere dati della dimensione originale
Imputazione multipla con bootstrap
Imputazione bootstrap: pro e contro
Pro:
- Funziona con qualsiasi metodo di imputazione.
- Può approssimare quantità difficili da calcolare analiticamente.
- Funziona con dati MCAR e MAR.
Contro:
- Lento con molte repliche o calcoli pesanti.
Bootstrap in pratica
calc_correlation <- function(data, indices) {
# Restituisci il coefficiente di correlazione
return(corr_coeff)
}
Bootstrap in pratica
calc_correlation <- function(data, indices) {
# Ottieni il campione bootstrap
data_boot <- data[indices, ]
# Restituisci il coefficiente di correlazione
return(corr_coeff)
}
Bootstrap in pratica
calc_correlation <- function(data, indices) {
# Ottieni il campione bootstrap
data_boot <- data[indices, ]
# Imputa con kNN
data_imp <- kNN(data_boot)
# Restituisci il coefficiente di correlazione
return(corr_coeff)
}
Bootstrap in pratica
calc_correlation <- function(data, indices) {
# Ottieni il campione bootstrap
data_boot <- data[indices, ]
# Imputa con kNN
data_imp <- kNN(data_boot)
# Calcola la correlazione tra Weight e TotChol
corr_coeff <- cor(data_imp$Weight, data_imp$TotChol)
# Restituisci il coefficiente di correlazione
return(corr_coeff)
}
Bootstrap in pratica
library(boot)
boot_results <- boot(nhanes, statistic = calc_correlation, R = 50)
print(boot_results)
BOOTSTRAP NON PARAMETRICO ORDINARIO
Call:
boot(data = nhanes, statistic = calc_correlation, R = 50)
Statistiche bootstrap:
originale bias errore std.
t1* 0.03028306 0.007385452 0.04207152
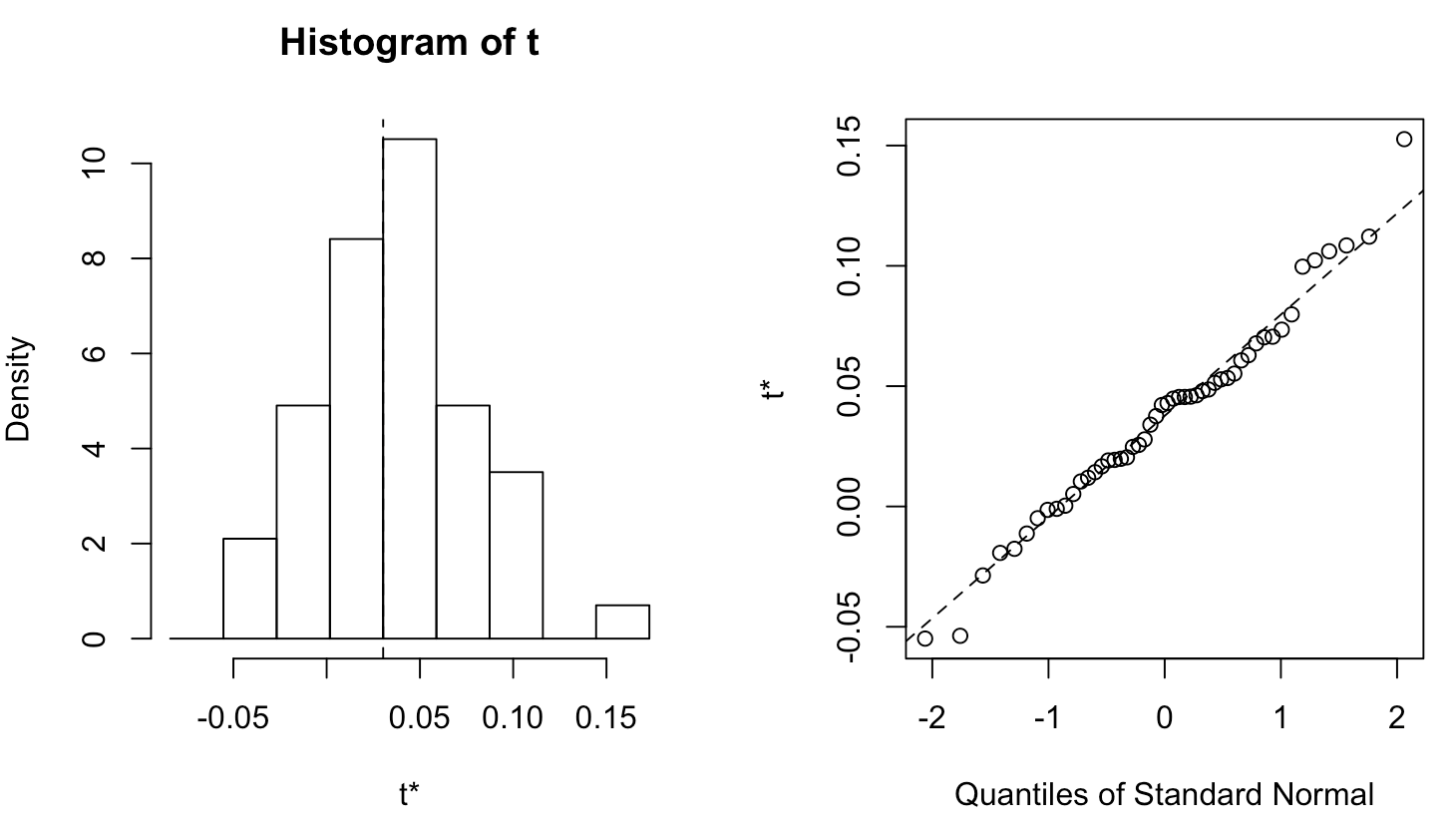
Grafico dei risultati bootstrap
plot(boot_results)
Intervalli di confidenza con bootstrap
boot_ci <- boot.ci(boot_results, conf = 0.95, type = "norm")
print(boot_ci)
CALCOLO DEGLI INTERVALLI DI CONFIDENZA BOOTSTRAP
Basato su 50 repliche bootstrap
CALL :
boot.ci(boot.out = boot_results, conf = 0.95, type = "norm")
Intervalli:
Livello Normale
95% (-0.0596, 0.1054 )
Calcoli e intervalli sulla scala originale
Esercitiamoci con il bootstrap!
Gestione dei dati mancanti con imputazioni in R

