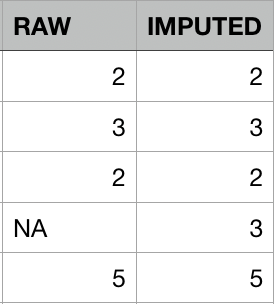
Imputazione con media
Gestione dei dati mancanti con imputazioni in R

Michal Oleszak
Machine Learning Engineer
Vocabolario: imputazione
Imputation = stimare in modo ragionato i valori mancanti
- Imputazione basata su donatore: si usano altre osservazioni complete per riempire i mancanti.
- Imputazione basata su modello: si prevedono i mancanti con un modello statistico o ML.
In questo capitolo vediamo metodi basati su donatore:
- Imputazione con media
- Hot-deck
- kNN
Imputazione con media
L’imputazione con media funziona bene per serie temporali che oscillano casualmente attorno a una media di lungo periodo.
Per dati trasversali è spesso una scelta pessima:
- Distrugge le relazioni tra variabili.
- I valori imputati non hanno varianza.
Imputazione con media: pratica
Obiettivo: imputare con la media Height e Weight nei dati NHANES.
- Crea indicatori binari che segnalino se il valore era mancante.
nhanes <- nhanes %>%
mutate(Height_imp = ifelse(is.na(Height), TRUE, FALSE)) %>%
mutate(Weight_imp = ifelse(is.na(Weight), TRUE, FALSE))
- Sostituisci i mancanti in
HeighteWeightcon le rispettive medie.
nhanes_imp <- nhanes %>%
mutate(Height = ifelse(is.na(Height), mean(Height, na.rm = TRUE), Height)) %>%
mutate(Weight = ifelse(is.na(Weight), mean(Weight, na.rm = TRUE), Weight))
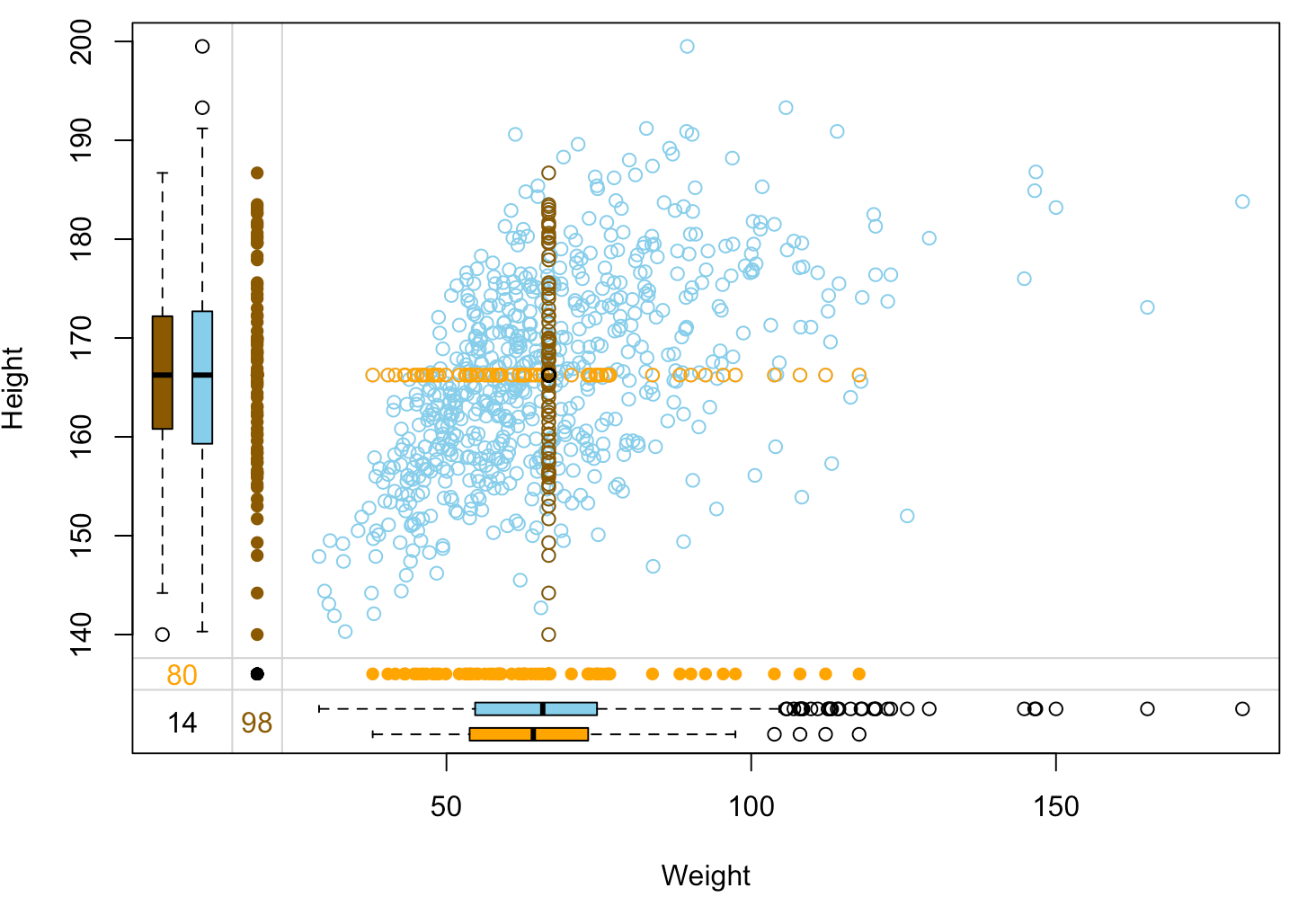
Dati NHANES imputati con media
nhanes_imp %>%
select(Weight, Height, Height_imp, Weight_imp) %>%
head()
Weight Height Height_imp Weight_imp
1 73.20000 166.2499 TRUE FALSE
2 72.30000 166.2499 TRUE FALSE
3 57.70000 158.9000 FALSE FALSE
4 88.90000 183.3000 FALSE FALSE
5 45.10000 157.6000 FALSE FALSE
6 66.77065 158.4000 FALSE TRUE
Valutare la qualità: margin plot
nhanes_imp %>% select(Weight, Height, Height_imp, Weight_imp) %>% marginplot(delimiter="imp")
Problemi con l’imputazione con media
Distrugge le relazioni tra variabili:
- Dopo aver imputato
HeighteWeightcon la media, la loro correlazione positiva si indebolisce. - I modelli che predicono una variabile dall’altra verranno ingannati dai valori imputati anomali e daranno risultati distorti.
Nessuna variabilità nei dati imputati:
- Con meno varianza, tutti gli errori standard sono sottostimati. Questo impedisce test d’ipotesi affidabili e il calcolo di intervalli di confidenza.
Imputazione con mediana e moda
- Invece della media, si può imputare con mediana o moda.
- La mediana è migliore in presenza di outlier.
- Per variabili categoriche non possiamo calcolare media o mediana, quindi usiamo la moda.
- Mediana e moda hanno gli stessi limiti della media.
Passiamo alla pratica !
Gestione dei dati mancanti con imputazioni in R

